gBlocksのqPCRコントロールとしての利用方法
執筆 IDT-MBL KK 矢野 実
IDT社のgBlocks Gene Fragments(以下gBlocks)は、お客様ご指定の配列を2本鎖DNA断片として合成、精製、納品するサービスです。安価かつ短納期の人工遺伝子合成サービスとして、全世界で好評を得ています。
gBlocksの用途として最も多いのは、遺伝子クローニングや変異体作製などのコンストラクト作製です。その他にin vitro transcriptionのテンプレート、CRISPR/Cas9用など様々な用途で使われていますが、あまり知られていないのがqPCRのコントロールとしての用途です。
gBlocksをコントロールとして用いれば、プライマー・プローブセットがターゲット領域を含む断片を正確に検出できているかどうかを定性的に確認出来ます。絶対定量やマルチプレックスqPCR実験をおこなうためにプライマー・プローブセットの検量線を作成する場合、およびその検量線を用いて増幅効率を計算する場合など、定量的な確認の際にも用いることが出来ます。
例えば、あるターゲット遺伝子用に用意したプライマー・プローブセットによってqPCR実験を行ったところシグナルが検出されなかった場合、検出されない原因がプライマー・プローブの設計にあるのか、あるいはそもそも検体にターゲット断片が含まれていなかったのかなど、原因を確認する必要があります。もしターゲット領域の断片が手元にあれば、それをコントロール断片としてqPCR実験を行い、検出の有無を定性的に確認し、原因を究明につなげることが可能です。
さらに、絶対定量を行う場合や、プライマーセットの増幅効率を確認する際には、検量線を作成する必要があります。そのためには、コピー数(モル数、あるいは質量と分子量)が明確な、ターゲット領域を含むコントロール断片が必要です。このコントロール断片を用いて希釈系列を作製し、それをテンプレートにしてqPCR実験行うことで、検量線の作成が可能です。gBlocksは分子量及び納品量が明確なため、容易に検量線を作成できます。
図1が、ヒトの内在性コントロール遺伝子HPRTとGUSについて、gBlocksで取得した断片で作製した希釈系列(101–107 copies)をテンプレートにしてqPCRを行って、検量線を作成した実験例になります。
gBlocksの用途として最も多いのは、遺伝子クローニングや変異体作製などのコンストラクト作製です。その他にin vitro transcriptionのテンプレート、CRISPR/Cas9用など様々な用途で使われていますが、あまり知られていないのがqPCRのコントロールとしての用途です。
gBlocksをコントロールとして用いれば、プライマー・プローブセットがターゲット領域を含む断片を正確に検出できているかどうかを定性的に確認出来ます。絶対定量やマルチプレックスqPCR実験をおこなうためにプライマー・プローブセットの検量線を作成する場合、およびその検量線を用いて増幅効率を計算する場合など、定量的な確認の際にも用いることが出来ます。
例えば、あるターゲット遺伝子用に用意したプライマー・プローブセットによってqPCR実験を行ったところシグナルが検出されなかった場合、検出されない原因がプライマー・プローブの設計にあるのか、あるいはそもそも検体にターゲット断片が含まれていなかったのかなど、原因を確認する必要があります。もしターゲット領域の断片が手元にあれば、それをコントロール断片としてqPCR実験を行い、検出の有無を定性的に確認し、原因を究明につなげることが可能です。
さらに、絶対定量を行う場合や、プライマーセットの増幅効率を確認する際には、検量線を作成する必要があります。そのためには、コピー数(モル数、あるいは質量と分子量)が明確な、ターゲット領域を含むコントロール断片が必要です。このコントロール断片を用いて希釈系列を作製し、それをテンプレートにしてqPCR実験行うことで、検量線の作成が可能です。gBlocksは分子量及び納品量が明確なため、容易に検量線を作成できます。
図1が、ヒトの内在性コントロール遺伝子HPRTとGUSについて、gBlocksで取得した断片で作製した希釈系列(101–107 copies)をテンプレートにしてqPCRを行って、検量線を作成した実験例になります。
図1: gBlocksで取得した断片でを用いて検量線を作成した例
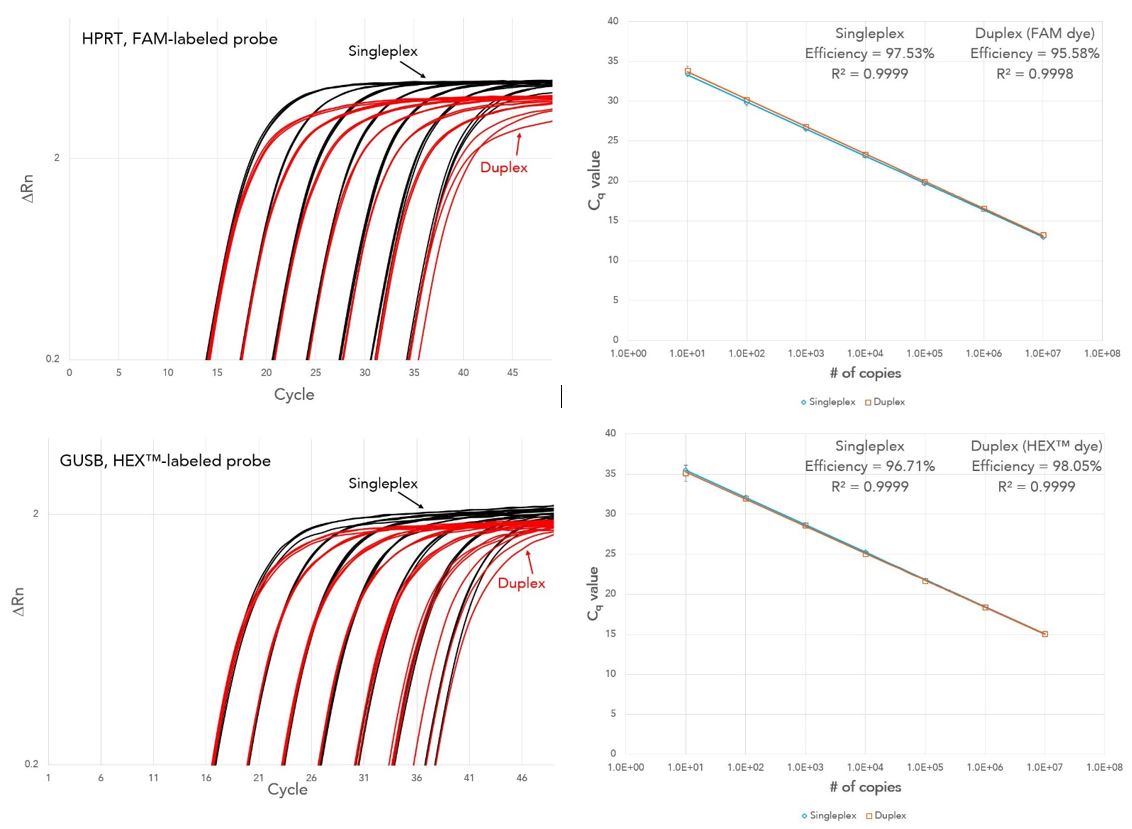
※ HPRT のAssay IDはHs.PT.58v.45621572、GUSB のAssay IDは Hs.PT.58v.27737538
※ 出典: https://www.idtdna.com/pages/products/qpcr-and-pcr/gene-expression/primetime-gene-expression-master-mix#performance_sq
※ >> Assay IDとは
これまで、コントロール断片を手に入れるには、cDNAライブラリなどからのクローニング作業が必要でした。しかしgBlocksを利用すれば、アンプリコンの配列情報を発注するだけで、手間がかかるクローニング作業を行う必要なしに、コントロールテンプレートを安価に短納期で入手できます。500bpであれば、1週間で納品できる事も多く、大変好評を頂いております。
>> 価格・納期はこちらをご覧下さい
またこの手軽さから、アンプリコンのみではなく遺伝子全体をコントロールテンプレートとして合成する事も可能です。
なお、gBlocksは125bp以上2kb以下という制限があるため、アンプリコンが125bp未満の場合は、「アンプリコンに前後の配列を加えた125bp以上の配列」をご発注ください。
IDT社のPrimeTime qPCR Assays(プレデザイン)をご注文頂いた場合は、納品時にプライマー及びプローブの配列が開示されますので、その配列を基に、コントロール用gBlocksをご発注頂けます。
応用例として、マルチプレックスqPCR実験の検証及び最適化にgBlocksを利用する方法をご紹介します。マルチプレックスでqPCR実験を行う際には、まず各ターゲット遺伝子用のプライマー・プローブセットがシングルプレックスでワークすることを確認します。次に、マルチプレックスにした際に、異なるターゲット遺伝子のプライマーやプローブが互いに干渉せずに、シングルプレックスと同様の結果が得られるかどうか?など、を検証する必要があります。この検証用にコントロールとしてもgBlocksが活用できます。
図2が、各アッセイのアンプリコンをタンデムに配置したコントロール用のgBlocksの設計です。この断片をgBlocksとして入手し、これをコントロール断片(サンプル)としたマルチプレックスqPCR実験を行います。このコントロール断片には各ターゲット遺伝子断片が1:1:1:1で含まれているので、この実験結果で4アッセイのCq値がほぼ同じとなった場合、各プライマーセットの増幅効率がほぼ同じであり、マルチプレックスに使用できる可能性が高いことが確認できます。
図2: マルチプレックスアッセイ、コントロール用gBlocksの例
●配列例
ACVR2B-LIMK1-ACVR1B-CDK7 wt
TCATACCTGCATGAGGATGTGCCCTGGTGCCGTGGCGAGGGCCACAAGCCGTCT
ATTGCCCACAGGGACTTTAAAAGTAAGAATGTATTGCTGAAGAGCGACCTCACA
GCCGTGCTGGCTGACTTTGGCTTGGtttttGAACATCATCCACCGAGACCTCAA
CTCCCACAACTGCCTGGTCCGCGAGAACAAGAATGTGGTGGTGGCTGACTTCGG
GCTGGCGCGTCTCATGGTGGACGAGAAGACTtttttGTATGTGATCAGAAGCTG
CGTCCCAACATCCCCAACTGGTGGCAGAGTTATGAGGCACTGCGGGTGATGGGG
AAGATGATGCGAGAGTGTTGGTATGtttttgGATGTATGGTGTAGGTGTGGACA
TGTGGGCTGTTGGCTGTATATTAGCAGAGTTACTTCTAAGGGTTCCTTTTTTGC
CAGGAGATTCAGACCTTGATCAGCTAACA
※ 4遺伝子のアンプリコンをタンデムに配置しました。
※ 各アンプリコンを明確にするため、アンプリコン間にtttttを配置しました。
※ この断片をクローニングしたい場合には、両末端にクローニング用の制限酵素認識部位の設定をお勧めします。
ACVR2B-LIMK1-ACVR1B-CDK7 wt
TCATACCTGCATGAGGATGTGCCCTGGTGCCGTGGCGAGGGCCACAAGCCGTCT
ATTGCCCACAGGGACTTTAAAAGTAAGAATGTATTGCTGAAGAGCGACCTCACA
GCCGTGCTGGCTGACTTTGGCTTGGtttttGAACATCATCCACCGAGACCTCAA
CTCCCACAACTGCCTGGTCCGCGAGAACAAGAATGTGGTGGTGGCTGACTTCGG
GCTGGCGCGTCTCATGGTGGACGAGAAGACTtttttGTATGTGATCAGAAGCTG
CGTCCCAACATCCCCAACTGGTGGCAGAGTTATGAGGCACTGCGGGTGATGGGG
AAGATGATGCGAGAGTGTTGGTATGtttttgGATGTATGGTGTAGGTGTGGACA
TGTGGGCTGTTGGCTGTATATTAGCAGAGTTACTTCTAAGGGTTCCTTTTTTGC
CAGGAGATTCAGACCTTGATCAGCTAACA
※ 4遺伝子のアンプリコンをタンデムに配置しました。
※ 各アンプリコンを明確にするため、アンプリコン間にtttttを配置しました。
※ この断片をクローニングしたい場合には、両末端にクローニング用の制限酵素認識部位の設定をお勧めします。
結果
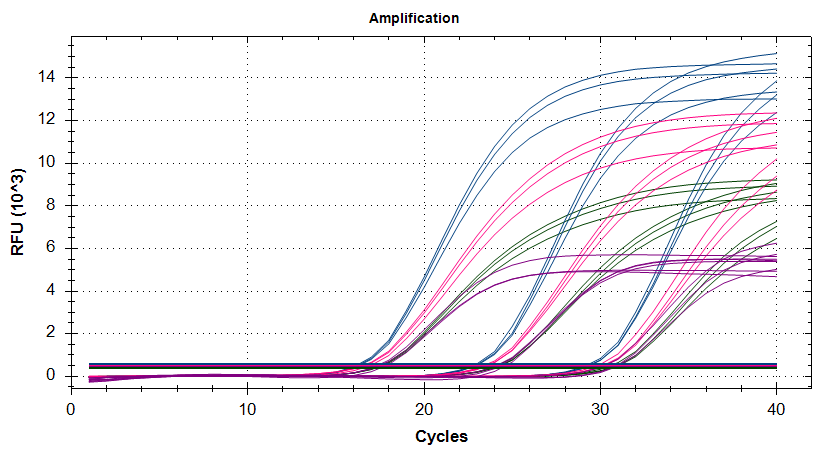
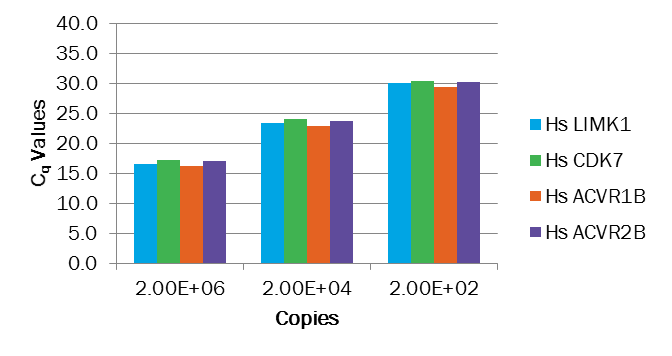
※ 4遺伝子のアッセイでほぼ同じCq値となりました。各遺伝子をターゲットにしたプライマーセットの増幅効率がほぼ同じであり、このアッセイ(プライマーとプローブのセット)がマルチプレックスに使用できる可能性が高いことが示されました。
※ 出典:http://sg.idtdna.com/pages/decoded/decoded-articles/synthetic-biology/decoded/2013/07/05/easily-designed-standard-curves-for-qpcr
このような設計のほかにも、研究者の皆様方のqPCR実験に合わせて、いろいろなコントロールを設定できます。ぜひご活用ください。
米国IDT社のDECODEDサイト(英語)にも、より詳細な情報がございます。合わせてご覧下さい。
https://sg.idtdna.com/pages/decoded/